一.原理介绍¶
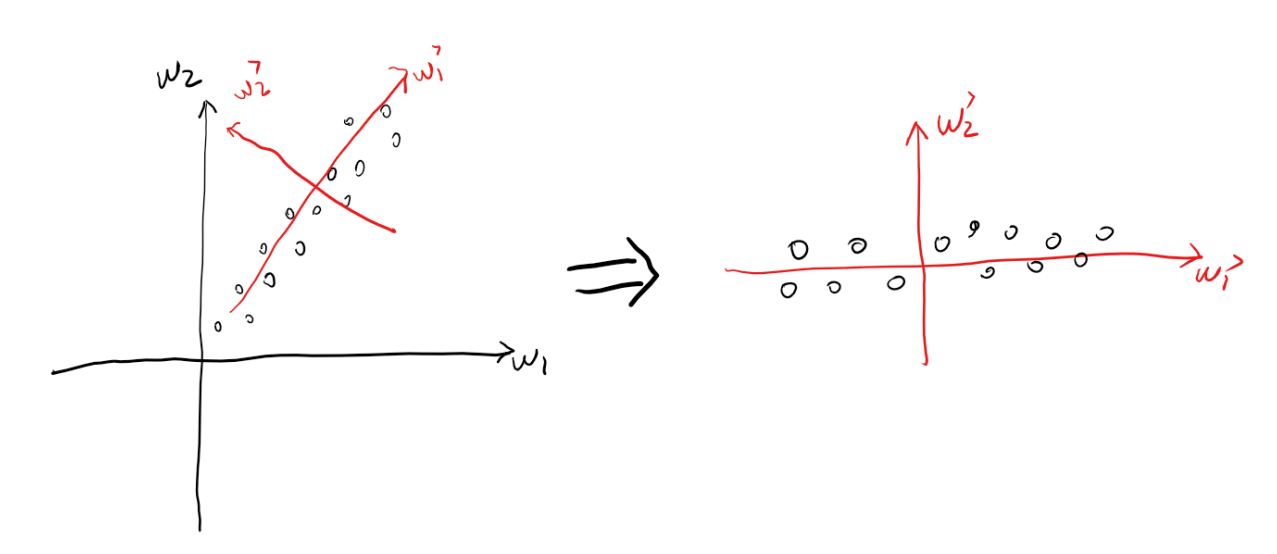
主成分分析想做的事如下图所示,将原始坐标系$<w_1,w_2>$变换为新的坐标系$<w'_1,w'_2>$,是的原始数据在新的坐标系下具有如下特点:
(1)在第一个坐标轴上的投影分散的尽可能的开(第一主成分),在第二个坐标轴上的投影其次(第二主成分)....
(2)新的坐标轴彼此正交,这样可以去掉变量间的相关性,如下面第一张图中数据几乎排在$y=x$这条线上,而经过pca的变换后,数据各维度失去了相关性
二.求解第一个坐标轴(第一主成分)¶
接下来让我们先从第一个坐标轴入手,根据我们的目标,我们要让原始的数据点$X\in R^{m\times n}$在某一个方向$w\in R^n$上的投影点尽可能的分散,这里涉及两个点:
(1)如果计算投影坐标;
(2)如何衡量分散程度;
下面依次推导
投影坐标的计算¶
抽样坐标的计算推导如下图,将某样本点$x$看做一个向量,将坐标轴方向向量$w$移动到与$x$相同的原点,假设两向量的夹角为$\theta$,在$w^Tw=1$的约束条件下,经过推导可得投影坐标可表示为$x^Tw$
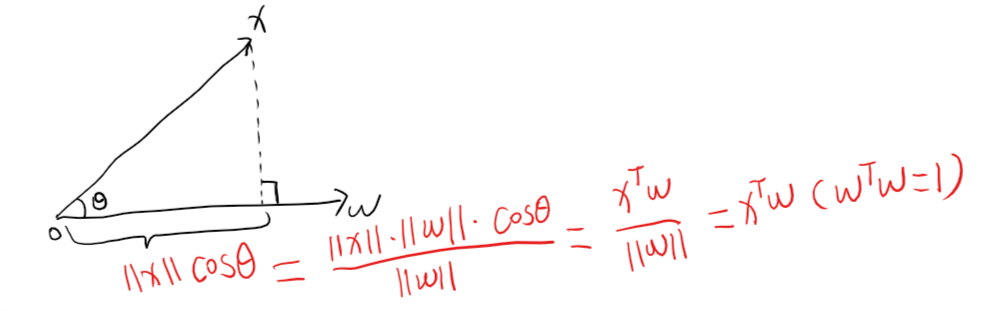
分散程度的衡量:方差¶
对于分散程度,显然最直接的一个参考指标可以使用方差,方差越大说明数据越分散,那么在坐标轴$w$上所有数据投影点的方差如下:
$$ S(X,w)=\sum_{i=1}^m(x_i^Tw-\bar{x}^Tw)^2 $$这里,$x_i\in R^n$,$\bar{x}=\frac{\sum_{i=1}^m x_i}{m}$,通常为了方便可以先进行去中心化的操作,即令$X$中的样本点都减去它每个维度的均值
$$ X=X-\bar{X} $$所以这时的方差就可以简单写作:
$$ S(X,w)=\sum_{i=1}^m(x_i^Tw)^2=\sum_{i=1}^m w^Tx_ix_i^Tw=w^T\sum_{i=1}^m (x_ix_i^T)w=w^T[x_1,x_2,...,x_m]\cdot\begin{bmatrix} x_1^T\\ x_2^T\\ ...\\ x_m^T \end{bmatrix}w=w^TX^TXw $$所以,我们我们要求最优$w^*$便是
$$ w^*=arg\max_{w}w^TX^TXw $$这依赖于$X^TX$的性质
三.基于$X^TX$求解前$k$个主成分¶
由于$X^TX$为实对称矩阵,我们可以对其进行正交分解,且其特征值均大于等于0,所以我们可以将$X^TX$分解为如下形式:
$$ X^TX=U\Lambda U^T=[u_1,u_2,...,u_n]\begin{bmatrix} \lambda_1 & 0 & 0 & 0 \\ 0 & \lambda_2 & 0 & 0\\ 0 & 0 & \ddots & 0\\ 0 & 0 & 0 & \lambda_n \end{bmatrix}\begin{bmatrix} u_1^T\\ u_2^T\\ ...\\ u_n^T \end{bmatrix} $$其中,$\lambda_1\geq\lambda_2\geq\cdots\geq\lambda_n\geq 0,u_i^Tu_j=\left\{\begin{matrix} 1 &i=j \\ 0 &i\neq j \end{matrix}\right. $
对于,任意$w(s.t. w^Tw=1)$,都有:
$$ w^TX^TXw=(w^Tu_1)^2\lambda_1+(w^Tu_2)^2\lambda_2+\cdots+(w^Tu_n)^2\lambda_n $$由于$u_1,u_2,...,u_n$彼此正交,且为单位向量,所以$(w^Tu_1)^2+(w^Tu_2)^2+\cdots+(w^Tu_n)^2=1$,所以结果也就可以看出来了:
(1)对于第一个坐标轴(第一主成分),即是$\lambda_1$对应的特征向量$u_1$...
(2)对于第二个坐标轴(第二主成分),即是$\lambda_2$对应的特征向量$u_2$...
(3)......
通常,我们选择前$k$个坐标轴进行映射$U_k=[u_1,u_2,...,u_k]$,生成的新数据为$X_k=XU_k$
import numpy as np
#造伪样本
X=np.linspace(0,10,100)
Y=3*X+2
X+=np.random.normal(size=(X.shape))*0.3#添加噪声
data=np.c_[X,Y]
import matplotlib.pyplot as plt
%matplotlib inline
plt.scatter(data[:,0],data[:,1])
plt.xlabel('x')
plt.ylabel('y')
Text(0,0.5,'y')
去中心化¶
data=data-np.mean(data,axis=0,keepdims=True)
求$X^TX$¶
xTx=data.T.dot(data)
正交分解¶
eig_vals,eig_vecs=np.linalg.eig(xTx)
eig_vals
array([8.27256772e+00, 8.50444256e+03])
eig_vecs
array([[-0.94847792, -0.31684323],
[ 0.31684323, -0.94847792]])
校验一下特征分解结果
eig_vecs.dot(np.diag(eig_vals)).dot(eig_vecs.T)-xTx
array([[ 1.25055521e-12, 0.00000000e+00],
[ 0.00000000e+00, -9.09494702e-13]])
由于np.linalg.eig的特征值并未按从大到小的顺序排序,所以我们需要进行一下重排
sorted_indice=np.argsort(-1*eig_vals)#默认是升序排序
eig_vals=eig_vals[sorted_indice]
eig_vecs[:]=eig_vecs[:,sorted_indice]
现在的特征矩阵,第一列便是第一主成分,第二列便是第二主成分,接下来我们可以轻易拿到转换后的数据,只需要去中心化数据矩阵和特征矩阵相乘即可
new_data=data.dot(eig_vecs)
变化后的数据¶
plt.scatter(new_data[:,0],new_data[:,1])
plt.xlabel('x')
plt.ylabel('y')
plt.xlim(-20, 20)
plt.ylim(-20, 20)
(-20, 20)
可以发现,最终得到了我们想要的结果...,最后将代码整理一下,放到ml_models.decomposition.PCA中