library(tidyverse)
library(AER)
library(MASS)
library(broom)
library(nlme)
library(gmodels)
Modelos lineales: cómo aprender estadística
Original de: Jonas Kristoffer Lindeløv
Modificado y traducido por: Miguel Angel Núñez Ochoa

¿ Quién de ustedes ya ha llevado alguna clase de estadística ?
Un problema común cuando nos enseñan matemáticas (sobretodo estadística) es que en muchas ocasiones, terminamos memorizando fórmulas muchas formulas y sustituyendo valores, sin razonar qué es lo que significan las matemáticas que estamos utilizando, por ejemplo ¿ Ustedes sabían que muchos test estadísticos son regresiones lineales ? , si la respuesta es no, pues en este taller vamos a visitar la teoría de la regresión lineal y a partir de ahí visitaremos varios test estadísticos desde el framework de las regresiones lineales.
Entonces, en vez de hacerles aprender mil formulas, vamos a entender que que significa cada test, y al entender cada uno como un caso especial de la regresión lineal, será más fácil aprender los nombres de los casos específicos, que las formulas.
REFRESHER:
¿ Alguien reconoce las siguientes formulas ?
$$
\frac{1}{n} \cdot \sum_{i=1}^n x_i
$$$$
\frac{1}{n-1} \cdot\sum_{i=1}^n (x_i-\mu)^2
$$- ¿ Cuál es la intuición detrás de ellas ?
Regresión Lineal
La idea general de la regresión lineal es que queremos capturar la relación entre una variable dependiente $Y$ con una o más variables explicatorias $X_1,X_2,...,X_n$
Para comenzar con un ejemplo sencillo, consideraremos la relación entre calificaciones (Score) y la proporción promedio de alumnos por maestro (Student Teacher Ratio STR) de algunas escuelas ficticias (cuando en la regresión lineal solo existe una variable explicatoria, generalmente se le conoce como regresión lineal simple), dicha relación la queremos ajustar a una linea recta, formalmente:
$$ Y = a + b \cdot X $$De tal modo que queremos generar el siguiente modelo:
$$ Score \sim \beta_0 + \beta_1 \cdot STR + u_i $$Score <- c(680, 640, 670, 660, 630, 660, 635)
STR <- c(15, 17, 19, 20, 22, 23.5, 25)
Schools <- data.frame( Score = Score,
STR = STR)
head(Schools)
| Score | STR |
|---|---|
| 680 | 15.0 |
| 640 | 17.0 |
| 670 | 19.0 |
| 660 | 20.0 |
| 630 | 22.0 |
| 660 | 23.5 |
options(repr.plot.width=8, repr.plot.height=4) # controla tamaño de plot
ggplot(Schools, aes(y = Score, x = STR)) + geom_point() + geom_smooth(method = lm, se = F)
Ahora lo haremos con datos reales de escuela de los distritos de california en EUA y veremos cómo estimar, dichos coeficientes para generar la recta:
data(CASchools)
# TODO:
# Describir cuantas observaciones y cuantas variables tiene el Dataset
# Calcular el STR y agregarlo al dataset STR = alumnos / profesores
# Calcule el Score como el promedio de la calificación de lectura y matemáticas
# Genere los histogramas tanto de Score como de STR. HINT : geom_hist()
# Calcule la media y sd de Score y STR guardarla en una variable tipo avg_STR o sd_STR y reportarla
# Reportar la correlación entre Score y STR
# Graficar la regresión lineal entre Score y STR HINT: acabamos de ver como
ESTIMADOR OLS
El estimador de mínimos cuadrados ordinarios (OLS) trata de estimar los coeficientes $\beta_0$ y $\beta_1$ haciendo pasar la recta lo más cerca posible de todos los puntos, dicha distancia está medida por el cuadrado de los errores:
$$ \sum^n_{i = 1} (Y_i - \beta_0 - \beta_1 X_i)^2 $$Por lo tanto necesitamos encontrar $\beta_0$ y $\beta_1$ que:
- Minimicen
- Maximicen
La función de arriba.
Dicha optimización tiene la siguiente solución cerrada (closed-form solution: buscar en wiki si tienen curiosidad):
$$ \hat{\beta_1} = \frac{ \sum_{i = 1}^n (X_i - \overline{X})(Y_i - \overline{Y}) } { \sum_{i=1}^n (X_i - \overline{X})^2} $$$$ \hat{\beta_0} = \overline{Y} - \hat{\beta_1} \overline{X} $$# TODO
# Obtener con las formulas dadas B1 y B2 para la regresión Score ~ STR
Por suerte R tiene una función que calcula dicha regresión de forma automática más algunos diagnósticos, dicha función es lm(Y~X, data = data)
# TODO
# sustituir los valores necesarios para obtener la regresión Score ~ STR y asignarlos a la variable mdl
# obtener un resumen de dicho modelo a través de la función summary() y asignarla a mdl_smry
¿ Qué tan bueno es nuestro modelo?
Es la pregunta natual después de generar cualquier modelo, y para el caso de los modelos lineales tenemos dos mediciones que nos sirven de diagnóstico:
- Coeficiente de determinación: $R^2$
- Error estándar de la regresión: $RSE$
Coeficiente de detérminación
Describe que tanta varianza de la variable dependiente (Score) explica la variable independiente (STR)
Y se puede calcular de la siguiente forma:
$$ \begin{align} R^2 & = \frac{ESS}{TSS} \\ donde: \\ ESS & = \sum_{i = 1}^n \left( \hat{Y_i} - \overline{Y} \right)^2, \\ TSS & = \sum_{i = 1}^n \left( Y_i - \overline{Y} \right)^2, \\ \end{align} $$Pero dado que $ TSS = ESS + SSR $ podemos reescribir la expresión de $R^2$ como:
$$ \begin{align} R^2 = 1- \frac{SSR}{TSS} \\ SSR = \sum_{i=1}^n \hat{u}_i^2 \end{align} $$Es decir el coeficiente de determinación es una relación entre la suma cuadrada de los residuos y la suma cuadrata total (es decir, que tanto efectivamente explicamos satisfactoriamente $Y$ en relación a $X$, es fácil observar que para que $R^2 = 1$ necesitariamos no cometer errores $(SSR = 0)$ o en caso contrario $R^2 = 0$ sería resultado de no poder explicar nada $Y$ con $X$ es decir $ESS = 0$
# TODO calcular el coeficiente de determinación
SSR <- sum(mdl_smry$residuals^2) # Para poder correr esta linea tienen que haber generado y asignado el resumen del modelo
Error estándar de la regresión (RSE)¶
Ésta medición nos ayuda a describir en promedio que tanto está separada una predicción ( la recta ) de la variable dependiente ( Score )
y se puede calcular de la siguiente forma:
$$ RSE = \frac{SSR}{n - 2} $$# TODO calcular RSE
# Hint: nrows() cuenta el número de filas del dataset
Supuestos de OLS
Basicamente tenemos que cumplir con 3 supuestos:
- No existen desviaciones sistemáticas entre las observaciones y la recta lo que se cumpleo si: $E(u_i|X_i) = 0$
- Las observaciones de la $Y_i$ deben ser independientes entre ellas
- Los outliers (valores atípicos) son poco probables
Muchos Test estadísticos son regresiones lineales!
To do: ¿ Cuál es la diferencia entre un test paramétrico y uno no-parametrico?¶
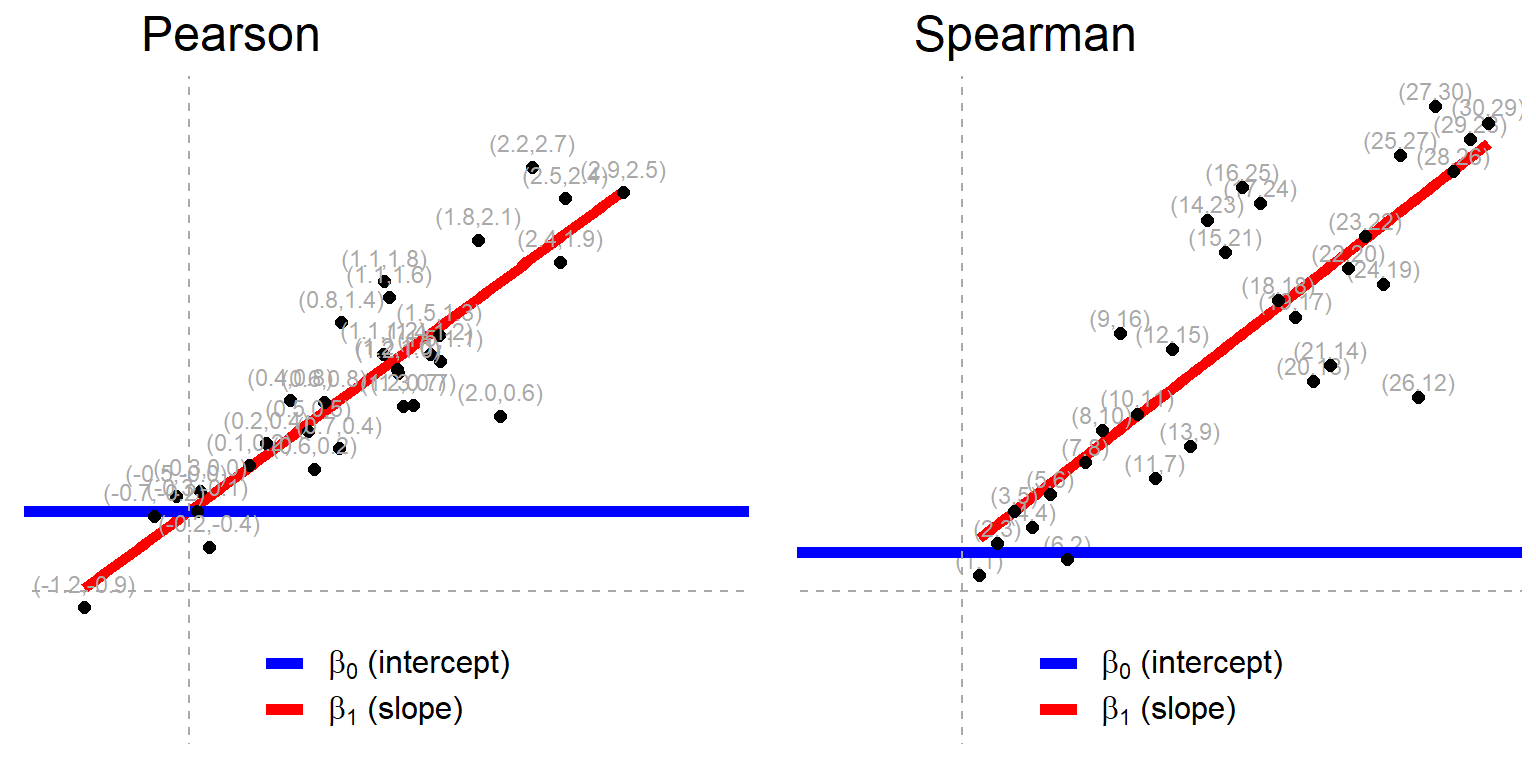
Correlación: Pearson y de Spearman¶
La correlación es una medida del grado de relación de dos variables siempre y cuando ambas sean cuantitativas y continuas, la correlación de pearson está descrita de la siguiente forma:
Pero en vez de verla como una formula separada la calcularemos como:
$$ Y \sim X $$Donde:
$\beta_1$: coeficiente de correlación de pearson
Siempre y cuando $Y$ y $X$ tengan la misma desviación estandar
cor.test(CASchools$Scores,CASchools$STR, method = "pearson") # Función hecha
tidy(summary(lm(CASchools$Scores ~ CASchools$STR))) # Modelo lineal equivalente: y = Beta0 + Beta1*x
tidy(summary(lm(scale(CASchools$Scores) ~ scale(CASchools$STR)))) # Sobre variables estandarizadas para recuperar Pearson por completo
Pearson's product-moment correlation
data: CASchools$Scores and CASchools$STR
t = -4.7513, df = 418, p-value = 2.783e-06
alternative hypothesis: true correlation is not equal to 0
95 percent confidence interval:
-0.3152213 -0.1335696
sample estimates:
cor
-0.2263627
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | 698.932949 | 9.4674911 | 73.824516 | 6.569846e-242 |
| CASchools$STR | -2.279808 | 0.4798255 | -4.751327 | 2.783308e-06 |
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | 6.543795e-16 | 0.04758525 | 1.375173e-14 | 1.000000e+00 |
| scale(CASchools$STR) | -2.263627e-01 | 0.04764200 | -4.751327e+00 | 2.783308e-06 |
Una nota sobre la aproximación lineal del coeficiente de pearson, es que los p-values son una aproximación apropiada para $n>10$ y casi perfecta para $n>20$
La versión no paramétrica del coeficiente de correlación de pearson, es la correlación de spearman la cúal evalúa la relación monótona entre dos variables continuas u ordinales.
Basicamente, la mayoría de los test estadísticos no-paramétricos, son exactamente los mismos que los paramétricos, pero a los datos les efectuamos una transformación llamada rank.
Rank transformation¶
la transformación rango es simplemente tomar una lista de números "reemplazarlos" con los enteros de su rango (1º más pequeño, 2º más pequeño, 3º más pequeño, etc.)
values = c(3.6, 3.4, -5.0, 8.2)
rank(values)
- 3
- 2
- 1
- 4
La transformación rango-signo es lo mismo pero hacemos la transformación sin los signos, y después se los agregamos:
signed_rank = function(x) sign(x) * rank(abs(x))
signed_rank(values)
- 2
- 1
- -3
- 4
Y como pueden intuir, la correlación de spearman la vamos a calcular
$$ rank(Y) \sim rank(X) $$cor.test(CASchools$Scores,CASchools$STR, method = "spearman") # Built-in
tidy(summary(lm(rank(CASchools$Scores) ~ rank(CASchools$STR)))) # modelo lineal equivalente
Warning message in cor.test.default(CASchools$Scores, CASchools$STR, method = "spearman"): "Cannot compute exact p-value with ties"
Spearman's rank correlation rho
data: CASchools$Scores and CASchools$STR
S = 14948000, p-value = 1.352e-05
alternative hypothesis: true rho is not equal to 0
sample estimates:
rho
-0.2105775
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | 254.8265249 | 11.61517976 | 21.939094 | 1.525150e-71 |
| rank(CASchools$STR) | -0.2105773 | 0.04781483 | -4.404017 | 1.351588e-05 |
se le conoce como ** ties ** a cuando tenemos dos valores identicos en los datos
Comparación de una media: T-test de una muestra y Wilcoxon de signo-rango¶
Es un procedimiento estadístico utilizado para determinar si $n$ observaciones podrían haber sido generadas por un distribución con con una media específica.
El modelo lineal equivalente del t-test es el siguiente:
$$ y = \beta_0 \qquad \mathcal{H}_0: \beta_0 = 0 $$el de la prueba de rangos con signo de wilcoxon
$$ signedrank(y) = \beta_0 \qquad \mathcal{H}_0: \beta_0 = 0 $$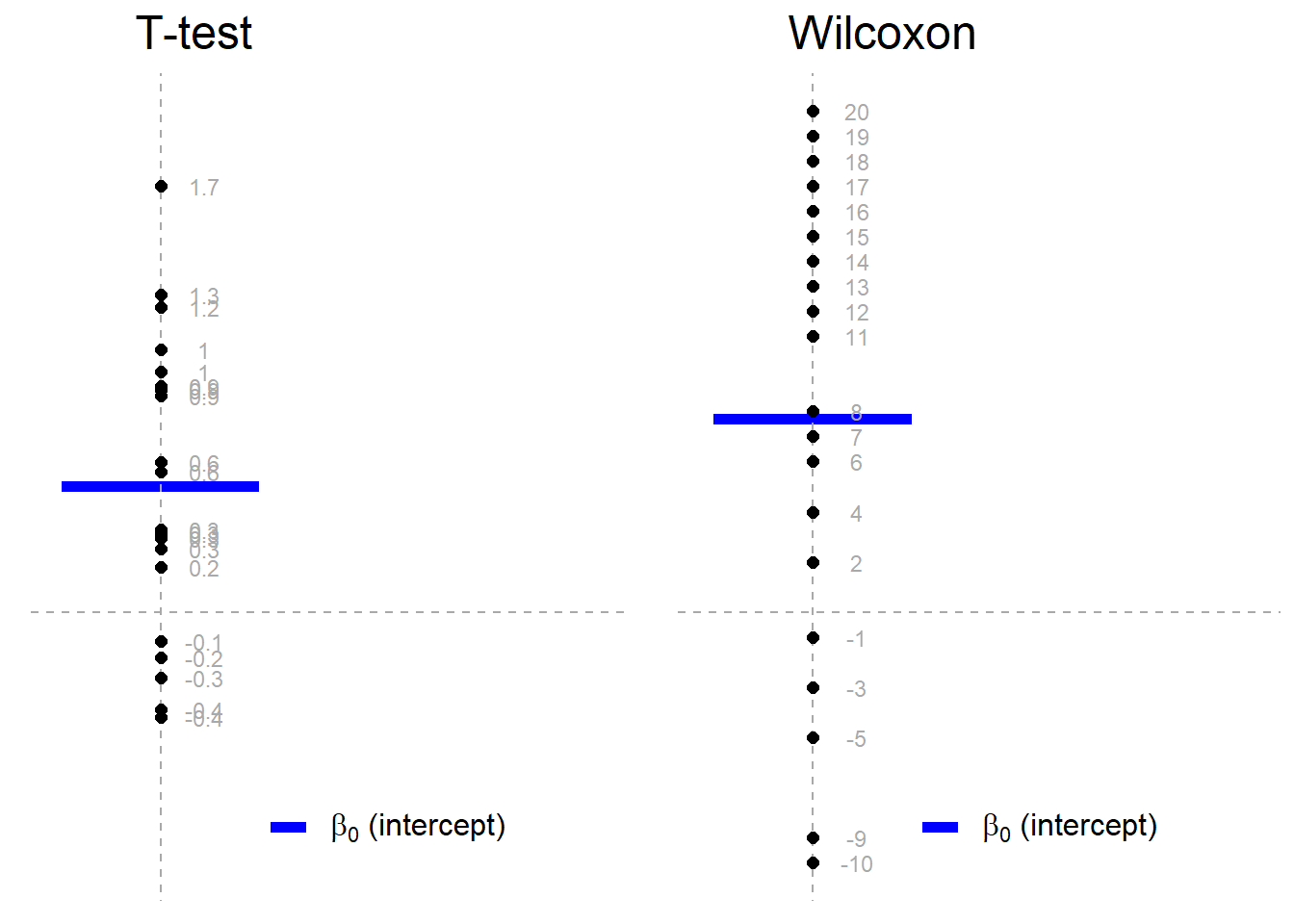
t.test(CASchools$Scores)
# Equivalent linear model: intercept-only
tidy(summary(lm(CASchools$Scores ~ 1)))
One Sample t-test data: CASchools$Scores t = 703.61, df = 419, p-value < 2.2e-16 alternative hypothesis: true mean is not equal to 0 95 percent confidence interval: 652.3291 655.9840 sample estimates: mean of x 654.1565
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | 654.1565 | 0.9297081 | 703.615 | 0 |
t.test(CASchools$Scores)
# Equivalent linear model: intercept-only
tidy(summary(lm(CASchools$Scores ~ 1)))
# Built-in
wilcox.test(CASchools$Scores)
# Equivalent linear model
tidy(summary(lm(signed_rank(CASchools$Scores) ~ 1))) # mismo modelo, solo con signed_rank
# Bonus:
t.test(signed_rank(CASchools$Scores))
Wilcoxon signed rank test with continuity correction data: CASchools$Scores V = 88410, p-value < 2.2e-16 alternative hypothesis: true location is not equal to 0
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | 210.5 | 5.923111 | 35.53876 | 1.568749e-128 |
One Sample t-test
data: signed_rank(CASchools$Scores)
t = 35.539, df = 419, p-value < 2.2e-16
alternative hypothesis: true mean is not equal to 0
95 percent confidence interval:
198.8573 222.1427
sample estimates:
mean of x
210.5
Esta aproximación es lo suficientemente buena cuando el tamaño de la muestra es mayor que 14 y casi perfecta si el tamaño de la muestra es mayor que 50
Dos medias y un grupo : Paired samples t-test and Wilcoxon matched pairs¶
Este tipo de pruebas se usan para comparar dos medias de población donde se tiene dos muestras en las que las observaciones en una muestra se pueden emparejar con las observaciones en la otra muestra (ejemplos ?)
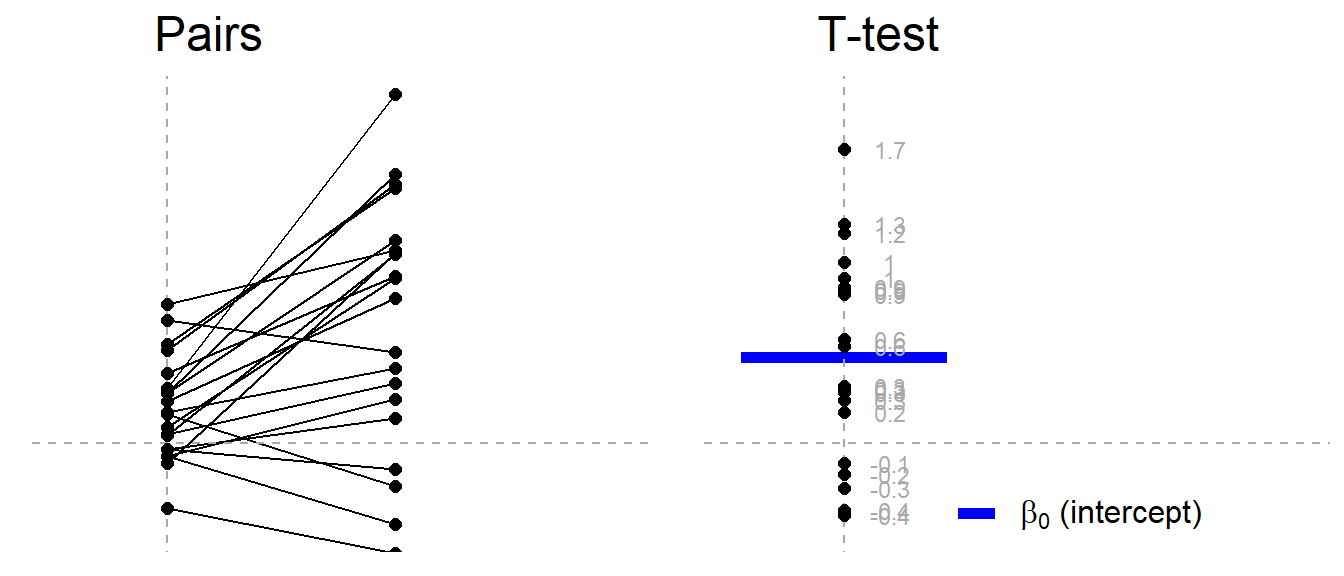
La aproximación lineal es bastante sencilla:
$$ y_2-y_1 = \beta_0 \qquad \mathcal{H}_0: \beta_0 = 0 $$y pueden estar seguros que la versión no paramétrica no es otra que:
$$ signedrank(y_2-y_1) = \beta_0 \qquad \mathcal{H}_0: \beta_0 = 0 $$Supongamos que tenemos un grupo de pacientes, a los que les vamos a dar una pastilla que hace inteligente a las personas, medimos el IQ antes y después de la pastilla, queremos comparar si la pastilla tiene un efecto sobre el IQ.
¿Qué supuesto del OLS viola en principio este problema y por lo tanto se tienen que utilizar muestras pareadas?
IQ_antes <- c(100,115,90,80,75)
IQ_despues <- c(101,110,95,99,105)
t.test(IQ_antes, IQ_despues, paired = TRUE) # Built-in paired t-test
tidy(summary(lm(IQ_antes - IQ_despues ~ 1))) # Equivalent linear model
Paired t-test
data: IQ_antes and IQ_despues
t = -1.5694, df = 4, p-value = 0.1916
alternative hypothesis: true difference in means is not equal to 0
95 percent confidence interval:
-27.690989 7.690989
sample estimates:
mean of the differences
-10
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | -10 | 6.371813 | -1.569412 | 0.1916352 |
# Built-in Wilcoxon matched pairs
wilcox.test(IQ_antes, IQ_despues, paired = TRUE)
# Equivalent linear model:
tidy(summary(lm(signed_rank(IQ_antes - IQ_despues) ~ 1)))
# Bonus: identical to one-sample t-test ong signed ranks
t.test(signed_rank(IQ_antes - IQ_despues))
Warning message in wilcox.test.default(IQ_antes, IQ_despues, paired = TRUE): "cannot compute exact p-value with ties"
Wilcoxon signed rank test with continuity correction data: IQ_antes and IQ_despues V = 2.5, p-value = 0.2228 alternative hypothesis: true location shift is not equal to 0
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | -2 | 1.313393 | -1.522774 | 0.202479 |
One Sample t-test
data: signed_rank(IQ_antes - IQ_despues)
t = -1.5228, df = 4, p-value = 0.2025
alternative hypothesis: true mean is not equal to 0
95 percent confidence interval:
-5.646562 1.646562
sample estimates:
mean of x
-2
Para muestras grandes $(N >> 100)$,la aproximación lineal del wolcoxon sign test es razonable, pero la aproximación no es muy precisa para muestras pequeñas.
Dos medias: Independent t-test and Mann-Whitney U¶
Utilizamos estos test, cuando tenemos dos grupos independientes diferenciados por un factor de interés, en este caso pensando en el ejemplo de la pastilla del IQ, en vez de tener solo un grupo de personas y medir antes y después de la pastilla, tenemos dos grupos de personas, uno al que le no le dimos pastilla (control) y otro al que sí (experimental).
la aproximación lineal de estos test, es la siguiente:
$$ y_i = \beta_0 + \beta_1 x_i \qquad \mathcal{H}_0: \beta_1 = 0 $$y la versión no paramétrica es conocida como Mann-Whitey U o Wilcoxon rank-sum test:
$$ rank(y_i) = \beta_0 + \beta_1 x_i \qquad \mathcal{H}_0: \beta_1 = 0 $$Para ambos casos la variable $x_i$ codifica si la observación pertenece al grupo control, o al grupo experimental.
La aproximación es apropiada cuando el tamaño de la muestra es mayor que 11 en cada grupo y virtualmente perfecto cuando $N> 30$ en cada grupo
df_IQ <- data.frame( IQ = c(IQ_antes,IQ_despues),
Grupo = c(rep(0,5),rep(1,5))
)
df_IQ
| IQ | Grupo |
|---|---|
| 100 | 0 |
| 115 | 0 |
| 90 | 0 |
| 80 | 0 |
| 75 | 0 |
| 101 | 1 |
| 110 | 1 |
| 95 | 1 |
| 99 | 1 |
| 105 | 1 |
tidy(summary(lm(df_IQ$IQ ~ df_IQ$Grupo)))
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | 92 | 5.389805 | 17.069263 | 1.409745e-07 |
| df_IQ$Grupo | 10 | 7.622336 | 1.311934 | 2.259355e-01 |
- ¿Cuál es la media del grupo control?
- ¿Cuál es la media del grupo experimental?
- ¿Cuál es la diferencia entre los dos grupos?
tidy(summary(lm(rank(df_IQ$IQ) ~ df_IQ$Grupo)))
| term | estimate | std.error | statistic | p.value |
|---|---|---|---|---|
| (Intercept) | 4.4 | 1.326650 | 3.316625 | 0.01059317 |
| df_IQ$Grupo | 2.2 | 1.876166 | 1.172604 | 0.27468613 |
La prueba t asume varianzas iguales para ambos grupos, existe un test que es exactamente igual que no asume esto, se conoce como WELCH t-test
y en la aproximación lineal solo especificamos que las varianzas son distintas por grupo:
nlme::gls(IQ ~ Grupo, data = df_IQ, weights = nlme::varIdent(form=~1|Grupo), method="ML")
Generalized least squares fit by maximum likelihood
Model: IQ ~ Grupo
Data: df_IQ
Log-likelihood: -35.69249
Coefficients:
(Intercept) Grupo
92 10
Variance function:
Structure: Different standard deviations per stratum
Formula: ~1 | Grupo
Parameter estimates:
0 1
1.0000000 0.3579878
Degrees of freedom: 10 total; 8 residual
Residual standard error: 14.3527
Tres o más medias: ANOVA de una vía y Kruskal-Wallis¶
La extensión para más grupos del t-test y el U-MannWhitney, se les conoce como ANOVA y Kruskal-Wallis, respectivamente.
La versión de los test, desde la aproximación lineal es la siguiente:
$$ y = \beta_0 + \beta_1 x_1 + \beta_2 x_2 + \beta_3 x_3 +... \qquad \mathcal{H}_0: y = \beta_0 $$Y no les sorprenderá que la versión no paramétrica (Kruskal-Wallis) es con una transformación rank sobre la variable dependiente.
Como pueden observar, en este momento ya pasamos de hablar de una regresión lineal simple, a una regresión lineal multiple.
Del mismo modo, las variables $x_1,x_2,....x_n$ son variables indicadoras.
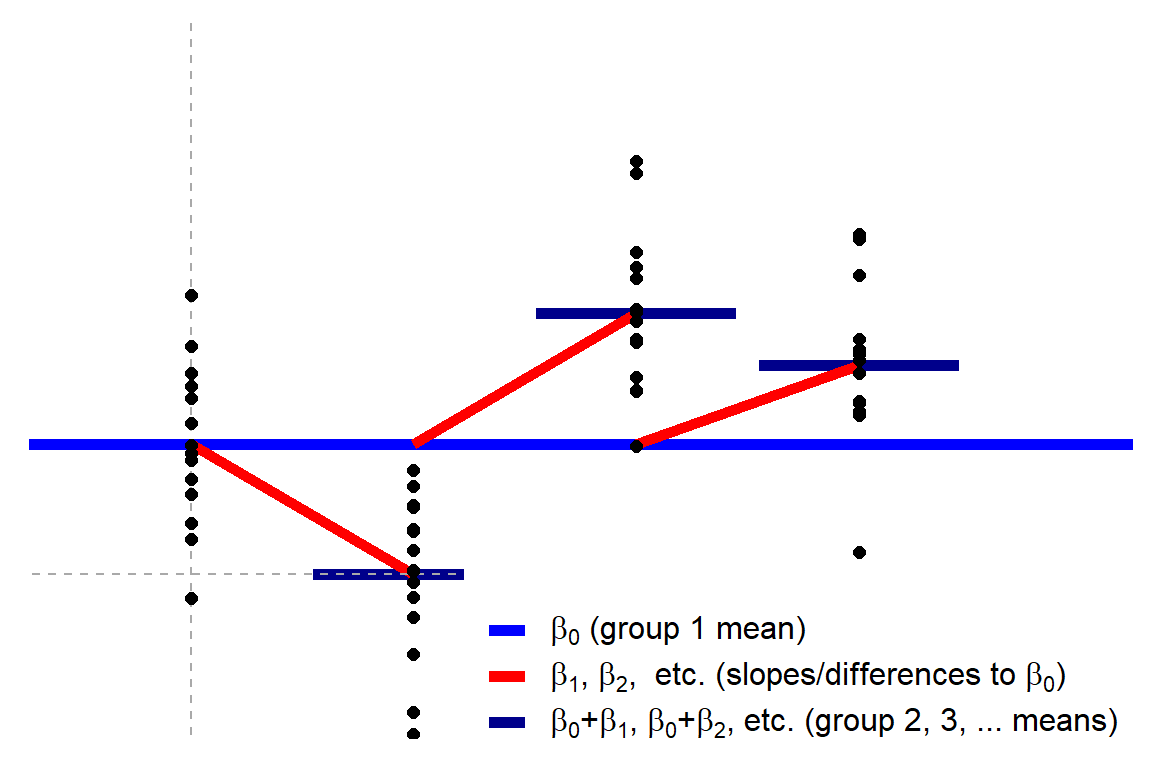
#Generar datos ficticios
N = 20 # Number of samples
D = data.frame(
value = c(rnorm(N, 0), rnorm(N, 1), rnorm(N, 0.5)),
group = rep(c('a', 'b', 'c'), each = N),
# Explicitly add indicator/dummy variables
# Could also be done using model.matrix(~D$group)
#group_a = rep(c(1, 0, 0), each=N), # This is the intercept. No need to code
group_b = rep(c(0, 1, 0), each = N),
group_c = rep(c(0, 0, 1), each = N)
) # N of each level
D
| value | group | group_b | group_c |
|---|---|---|---|
| -0.79837608 | a | 0 | 0 |
| -2.10980476 | a | 0 | 0 |
| -1.16688190 | a | 0 | 0 |
| 0.83424569 | a | 0 | 0 |
| 0.22914871 | a | 0 | 0 |
| 0.49672345 | a | 0 | 0 |
| 0.48576442 | a | 0 | 0 |
| -0.76534301 | a | 0 | 0 |
| 0.37214721 | a | 0 | 0 |
| -0.44297033 | a | 0 | 0 |
| -1.56068580 | a | 0 | 0 |
| -0.49685546 | a | 0 | 0 |
| -0.86609766 | a | 0 | 0 |
| -0.62627788 | a | 0 | 0 |
| 0.93813831 | a | 0 | 0 |
| -0.75546585 | a | 0 | 0 |
| 0.34198586 | a | 0 | 0 |
| -0.49379340 | a | 0 | 0 |
| -1.39684469 | a | 0 | 0 |
| -0.11642183 | a | 0 | 0 |
| 1.00168951 | b | 1 | 0 |
| 0.07937425 | b | 1 | 0 |
| 2.04035214 | b | 1 | 0 |
| 0.26562288 | b | 1 | 0 |
| 2.57094201 | b | 1 | 0 |
| 1.95303508 | b | 1 | 0 |
| 0.53978271 | b | 1 | 0 |
| 0.67015241 | b | 1 | 0 |
| 0.81970330 | b | 1 | 0 |
| -0.79491813 | b | 1 | 0 |
| 0.15997967 | b | 1 | 0 |
| 1.85665133 | b | 1 | 0 |
| 1.79281115 | b | 1 | 0 |
| 1.59885741 | b | 1 | 0 |
| -0.80518448 | b | 1 | 0 |
| 1.74835661 | b | 1 | 0 |
| 2.06647758 | b | 1 | 0 |
| 2.13948629 | b | 1 | 0 |
| 2.37452116 | b | 1 | 0 |
| 1.90445069 | b | 1 | 0 |
| -0.74199652 | c | 0 | 1 |
| -0.64953381 | c | 0 | 1 |
| 0.49907252 | c | 0 | 1 |
| 1.75670897 | c | 0 | 1 |
| 0.67682439 | c | 0 | 1 |
| 2.28548841 | c | 0 | 1 |
| 0.22978489 | c | 0 | 1 |
| 0.74287109 | c | 0 | 1 |
| 0.97999743 | c | 0 | 1 |
| -0.21285284 | c | 0 | 1 |
| 2.27330165 | c | 0 | 1 |
| 1.34576758 | c | 0 | 1 |
| -1.78778507 | c | 0 | 1 |
| 0.37547863 | c | 0 | 1 |
| 0.71141747 | c | 0 | 1 |
| 0.68241756 | c | 0 | 1 |
| 0.72096885 | c | 0 | 1 |
| 0.77019841 | c | 0 | 1 |
| 0.77680611 | c | 0 | 1 |
| -0.45616270 | c | 0 | 1 |
Anova(aov(value ~ group, D))
summary(lm(value ~ group_b + group_c, data = D))
| Sum Sq | Df | F value | Pr(>F) | |
|---|---|---|---|---|
| group | 25.69550 | 2 | 14.11414 | 1.049053e-05 |
| Residuals | 51.88568 | 57 | NA | NA |
Call:
lm(formula = value ~ group_b + group_c, data = D)
Residuals:
Min 1Q Median 3Q Max
-2.3367 -0.5615 0.1307 0.7411 1.7366
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) -0.3949 0.2133 -1.851 0.06936 .
group_b 1.5940 0.3017 5.283 2.07e-06 ***
group_c 0.9438 0.3017 3.128 0.00277 **
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1
Residual standard error: 0.9541 on 57 degrees of freedom
Multiple R-squared: 0.3312, Adjusted R-squared: 0.3077
F-statistic: 14.11 on 2 and 57 DF, p-value: 1.049e-05
kruskal.test(value ~ group, D) # Built-in
summary(lm(rank(value) ~ 1 + group_b + group_c, D)) # As linear model
Anova(aov(rank(value) ~ group, D)) # The same model, using a dedicated ANOVA function. It just wraps lm.
Kruskal-Wallis rank sum test data: value by group Kruskal-Wallis chi-squared = 18.62, df = 2, p-value = 9.051e-05
Call:
lm(formula = rank(value) ~ 1 + group_b + group_c, data = D)
Residuals:
Min 1Q Median 3Q Max
-34.00 -10.05 2.25 11.01 25.45
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) 17.550 3.287 5.339 1.69e-06 ***
group_b 23.450 4.648 5.045 4.93e-06 ***
group_c 15.400 4.648 3.313 0.00161 **
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1
Residual standard error: 14.7 on 57 degrees of freedom
Multiple R-squared: 0.3156, Adjusted R-squared: 0.2916
F-statistic: 13.14 on 2 and 57 DF, p-value: 2.025e-05
| Sum Sq | Df | F value | Pr(>F) | |
|---|---|---|---|---|
| group | 5679.1 | 2 | 13.1419 | 2.025152e-05 |
| Residuals | 12315.9 | 57 | NA | NA |
Todas éstas aproximaciones son lo suficientemente buenas para $n>12$
Las interacciones entre dos variables se pueden modelar con una multiplicación entre las variables indicadoras, lo que convierte al ANOVA de una vía en un ANOVA de dos (más) vias.
ANOVA de dos vías¶
$$ y = \beta_0 + \beta_1 X_1 + \beta_2 X_2 + \beta_3 X_1 X_2 \qquad \mathcal{H}_0: \beta_3 = 0 $$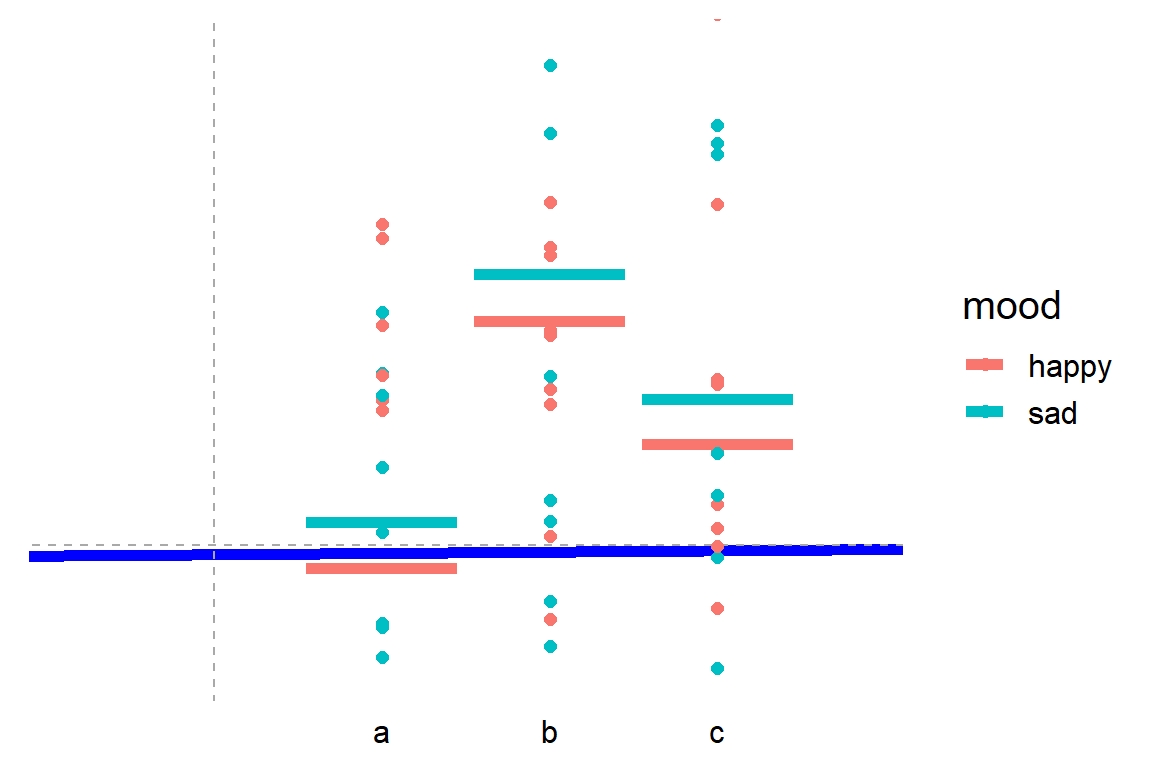
# Crossing factor
D$mood = c('happy', 'sad')
# Dummy coding
D$mood_happy = ifelse(D$mood == 'happy', 1, 0)
head(D)
| value | group | group_b | group_c | mood | mood_happy |
|---|---|---|---|---|---|
| -0.7983761 | a | 0 | 0 | happy | 1 |
| -2.1098048 | a | 0 | 0 | sad | 0 |
| -1.1668819 | a | 0 | 0 | happy | 1 |
| 0.8342457 | a | 0 | 0 | sad | 0 |
| 0.2291487 | a | 0 | 0 | happy | 1 |
| 0.4967234 | a | 0 | 0 | sad | 0 |
Anova(aov(value ~ mood + group + mood:group, D))
# Testing the interaction terms as linear model.
full <- lm(value~group_b + group_c + mood_happy + group_b:mood_happy + group_c:mood_happy, D) # Full model
null <- lm(value~group_b + group_c + mood_happy, D) # Without interaction
anova(null, full) #same F, p, and Dfs
| Sum Sq | Df | F value | Pr(>F) | |
|---|---|---|---|---|
| mood | 0.0001934 | 1 | 2.027877e-04 | 9.886907e-01 |
| group | 25.6954959 | 2 | 1.347138e+01 | 1.794009e-05 |
| mood:group | 0.3853185 | 2 | 2.020110e-01 | 8.177006e-01 |
| Residuals | 51.5001645 | 54 | NA | NA |
| Res.Df | RSS | Df | Sum of Sq | F | Pr(>F) |
|---|---|---|---|---|---|
| 56 | 51.88548 | NA | NA | NA | NA |
| 54 | 51.50016 | 2 | 0.3853185 | 0.202011 | 0.8177006 |
summary(full)
Call:
lm(formula = value ~ group_b + group_c + mood_happy + group_b:mood_happy +
group_c:mood_happy, data = D)
Residuals:
Min 1Q Median 3Q Max
-2.22162 -0.57203 0.07203 0.71437 1.83946
Coefficients:
Estimate Std. Error t value Pr(>|t|)
(Intercept) -0.447596 0.308821 -1.449 0.153017
group_b 1.589703 0.436739 3.640 0.000611 ***
group_c 1.111634 0.436739 2.545 0.013807 *
mood_happy 0.105426 0.436739 0.241 0.810164
group_b:mood_happy 0.008574 0.617643 0.014 0.988975
group_c:mood_happy -0.335625 0.617643 -0.543 0.589093
---
Signif. codes: 0 '***' 0.001 '**' 0.01 '*' 0.05 '.' 0.1 ' ' 1
Residual standard error: 0.9766 on 54 degrees of freedom
Multiple R-squared: 0.3362, Adjusted R-squared: 0.2747
F-statistic: 5.469 on 5 and 54 DF, p-value: 0.000383
- ¿Cuál es la media del grupo a tristes y cual la media de los felices?
- La interacción fue significativa?
Proporciones: Chi-squared y Tablas de contingencia¶
TODO: Para qué se usa las pruebas:
- Goodness of fit
- Contingency tables
El modelo lineal es aproximar $log(y) = \beta_0 + \beta_i x_i$ dónde $x_i$ es una variable indicadora.
D = data.frame(mood = c('happy', 'sad', 'meh'),
FinishedExam = c(90, 60, 70))
# Dummy coding for the linear model
D$mood_happy = ifelse(D$mood == 'happy', 1, 0)
D$mood_sad = ifelse(D$mood == 'sad', 1, 0)
D
| mood | FinishedExam | mood_happy | mood_sad |
|---|---|---|---|
| happy | 90 | 1 | 0 |
| sad | 60 | 0 | 1 |
| meh | 70 | 0 | 0 |
chi <- chisq.test(D$FinishedExam)
chi
# As log-linear model, comparing to an intercept-only model
full = glm(FinishedExam ~ mood_happy + mood_sad, data = D, family = poisson())
null = glm(FinishedExam ~ 1, data = D, family = poisson())
anova(null, full, test = 'Chisq')
glm(FinishedExam ~ mood, data = D, family = poisson())
Chi-squared test for given probabilities data: D$FinishedExam X-squared = 6.3636, df = 2, p-value = 0.04151
| Resid. Df | Resid. Dev | Df | Deviance | Pr(>Chi) |
|---|---|---|---|---|
| 2 | 6.269709e+00 | NA | NA | NA |
| 0 | -1.287859e-14 | 2 | 6.269709 | 0.04350609 |
Call: glm(formula = FinishedExam ~ mood, family = poisson(), data = D)
Coefficients:
(Intercept) moodmeh moodsad
4.4998 -0.2513 -0.4055
Degrees of Freedom: 2 Total (i.e. Null); 0 Residual
Null Deviance: 6.27
Residual Deviance: -2.22e-15 AIC: 24.36
print( c('happy', 'sad', 'meh'))
print(chi$expected)
print(chi$observed)
[1] "happy" "sad" "meh" [1] 73.33333 73.33333 73.33333 [1] 90 60 70
TODO: que significan los coeficientes de la regresión poisson? HINTS: --------------v
log(90)
log(90)-log(60)
90*exp(-.405465)
log(90)- log(70)
90*exp(-.251314)
Entonces: ¿qué significa que la prueba sea significativa?
D = data.frame(
mood = c('happy', 'happy', 'happy', 'happy','sad', 'sad', 'sad', 'sad'),
smoke = c('S', 'NS', 'S','NS', 'NS', 'S', 'NS','S'),
Freq = c(140, 90, 128, 80, 30, 140, 80, 135)
)
D
| mood | smoke | Freq |
|---|---|---|
| happy | S | 140 |
| happy | NS | 90 |
| happy | S | 128 |
| happy | NS | 80 |
| sad | NS | 30 |
| sad | S | 140 |
| sad | NS | 80 |
| sad | S | 135 |
D_table <- D %>%
group_by(mood,smoke) %>%
summarize(totalsmoke = sum(Freq, na.rm = TRUE)) %>%
spread(key = mood, value = totalsmoke) %>% # Mood to columns
dplyr::select(-smoke) %>% # Remove sex column
as.matrix()
D_table
| happy | sad | |
|---|---|---|
| 1 | 170 | 110 |
| 2 | 268 | 275 |
1 : No fumar 2 : Si fuma
# Dummy coding of D for linear model (skipping mood=="sad" and gender=="female")
# We could also use model.matrix(D$Freq~D$mood*D$sex)
D$mood_happy = ifelse(D$mood == 'happy', 1, 0)
D$smk_yes = ifelse(D$smoke == 'S', 1, 0)
D
| mood | smoke | Freq | mood_happy | smk_yes |
|---|---|---|---|---|
| happy | S | 140 | 1 | 1 |
| happy | NS | 90 | 1 | 0 |
| happy | S | 128 | 1 | 1 |
| happy | NS | 80 | 1 | 0 |
| sad | NS | 30 | 0 | 0 |
| sad | S | 140 | 0 | 1 |
| sad | NS | 80 | 0 | 0 |
| sad | S | 135 | 0 | 1 |
chisq.test(D_table)
# Using glm to do a log-linear model, we get identical results when testing the interaction term:
full = glm(Freq ~ 1 + mood_happy + smk_yes + mood_happy*smk_yes, data = D, family = poisson())
null = glm(Freq ~ 1 + mood_happy + smk_yes, data = D, family = poisson())
anova(null, full, test = 'Chisq')
# Note: let glm do the dummy coding for you
full = glm(Freq ~ mood * smoke, family = poisson(), data = D)
anova(full, test = 'Chisq')
# Note: even simpler syntax using MASS:loglm ("log-linear model")
MASS::loglm(Freq ~ mood + smoke, D)
Pearson's Chi-squared test with Yates' continuity correction data: D_table X-squared = 9.1232, df = 1, p-value = 0.002524
| Resid. Df | Resid. Dev | Df | Deviance | Pr(>Chi) |
|---|---|---|---|---|
| 5 | 34.43193 | NA | NA | NA |
| 4 | 24.79979 | 1 | 9.632149 | 0.001912008 |
| Df | Deviance | Resid. Df | Resid. Dev | Pr(>Chi) | |
|---|---|---|---|---|---|
| NULL | NA | NA | 7 | 123.38467 | NA |
| mood | 1 | 3.415486 | 6 | 119.96919 | 6.458740e-02 |
| smoke | 1 | 85.537252 | 5 | 34.43193 | 2.273774e-20 |
| mood:smoke | 1 | 9.632149 | 4 | 24.79979 | 1.912008e-03 |
Call:
MASS::loglm(formula = Freq ~ mood + smoke, data = D)
Statistics:
X^2 df P(> X^2)
Likelihood Ratio 34.43193 5 1.953102e-06
Pearson 29.92802 5 1.523758e-05
Forma bonita:¶
CrossTable(D_table, chisq = T ,expected = T )
Cell Contents
|-------------------------|
| N |
| Expected N |
| Chi-square contribution |
| N / Row Total |
| N / Col Total |
| N / Table Total |
|-------------------------|
Total Observations in Table: 823
|
| happy | sad | Row Total |
-------------|-----------|-----------|-----------|
1 | 170 | 110 | 280 |
| 149.016 | 130.984 | |
| 2.955 | 3.362 | |
| 0.607 | 0.393 | 0.340 |
| 0.388 | 0.286 | |
| 0.207 | 0.134 | |
-------------|-----------|-----------|-----------|
2 | 268 | 275 | 543 |
| 288.984 | 254.016 | |
| 1.524 | 1.734 | |
| 0.494 | 0.506 | 0.660 |
| 0.612 | 0.714 | |
| 0.326 | 0.334 | |
-------------|-----------|-----------|-----------|
Column Total | 438 | 385 | 823 |
| 0.532 | 0.468 | |
-------------|-----------|-----------|-----------|
Statistics for All Table Factors
Pearson's Chi-squared test
------------------------------------------------------------
Chi^2 = 9.573964 d.f. = 1 p = 0.001973561
Pearson's Chi-squared test with Yates' continuity correction
------------------------------------------------------------
Chi^2 = 9.123154 d.f. = 1 p = 0.002523945
interpretar contribución a Chi-squared: Si una celda dada difiere notablemente de la frecuencia esperada, entonces la contribución de esa celda al chi-cuadrado general es grande.
Sin darnos cuenta...
Hemos visitado muchos test estadísticos
Todos como casos específicos de un modelo lineal
Así en vez de aprendernos formulas....
Tratamos de entender :)
Proyecto¶
Realizar el análisis exploratorio (gráficas, análisis descriptivo, análisis estadístico (test enseñados y/u otros)) del siguiente dataset: https://www.kaggle.com/russellyates88/suicide-rates-overview-1985-to-2016
- Las comparaciones hacerlas en relación a México
