Семинар 7. Визуализация данных. Знакомство с sklearn.¶
Обратите внимание, что на семинаре 22 марта будет проверочная работа.
import pandas as pd
import numpy as np
import scipy as sp
import pylab as plt
%matplotlib inline
Квартет Энскомба¶
Наборы данных имеют одинаковое среднее, дисперсию, коэффициент корреляции.
data = np.array([
[
[10.0, 8.0, 13.0, 9.0, 11.0, 14.0, 6.0, 4.0, 12.0, 7.0, 5.0],
[8.04, 6.95, 7.58, 8.81, 8.33, 9.96, 7.24, 4.26, 10.84, 4.82, 5.68]
],
[
[10.0, 8.0, 13.0, 9.0, 11.0, 14.0, 6.0, 4.0, 12.0, 7.0, 5.0],
[9.14, 8.14, 8.74, 8.77, 9.26, 8.10, 6.13, 3.10, 9.13, 7.26, 4.74]
],
[
[10.0, 8.0, 13.0, 9.0, 11.0, 14.0, 6.0, 4.0, 12.0, 7.0, 5.0],
[7.46, 6.77, 12.74, 7.11, 7.81, 8.84, 6.08, 5.39, 8.15, 6.42, 5.73]
],
[
[8.0, 8.0, 8.0, 8.0, 8.0, 8.0, 8.0, 19.0, 8.0, 8.0, 8.0],
[6.58, 5.76, 7.71, 8.84, 8.47, 7.04, 5.25, 12.50, 5.56, 7.91, 6.89]
]
])
%precision 2
for i in range(data.shape[0]):
print "MEAN: ", data[i].mean(axis=1), "STD: ", data[i].std(axis=1), "CORR: ", np.corrcoef(data[i])[0, 1]
MEAN: [ 9. 7.5] STD: [ 3.16 1.94] CORR: 0.816420516345 MEAN: [ 9. 7.5] STD: [ 3.16 1.94] CORR: 0.816236506 MEAN: [ 9. 7.5] STD: [ 3.16 1.94] CORR: 0.81628673949 MEAN: [ 9. 7.5] STD: [ 3.16 1.94] CORR: 0.816521436889
Кроме того, решение задачи линейной ререссии дает для них одно и тоже уравнение:
$y = 3 + 0.5x$
Что же будет если их визуализировать?
plt.figure(figsize=(16, 4))
for idx, X in enumerate(data):
plt.subplot(1, 4, idx + 1)
plt.scatter(X[0], X[1])
Корреляция между признаками¶
Иногда бывает удобно посмотреть (например, видно линейно зависимые признаки).
from sklearn import datasets
boston = datasets.load_boston()
print boston.DESCR
Boston House Prices dataset
Notes
------
Data Set Characteristics:
:Number of Instances: 506
:Number of Attributes: 13 numeric/categorical predictive
:Median Value (attribute 14) is usually the target
:Attribute Information (in order):
- CRIM per capita crime rate by town
- ZN proportion of residential land zoned for lots over 25,000 sq.ft.
- INDUS proportion of non-retail business acres per town
- CHAS Charles River dummy variable (= 1 if tract bounds river; 0 otherwise)
- NOX nitric oxides concentration (parts per 10 million)
- RM average number of rooms per dwelling
- AGE proportion of owner-occupied units built prior to 1940
- DIS weighted distances to five Boston employment centres
- RAD index of accessibility to radial highways
- TAX full-value property-tax rate per $10,000
- PTRATIO pupil-teacher ratio by town
- B 1000(Bk - 0.63)^2 where Bk is the proportion of blacks by town
- LSTAT % lower status of the population
- MEDV Median value of owner-occupied homes in $1000's
:Missing Attribute Values: None
:Creator: Harrison, D. and Rubinfeld, D.L.
This is a copy of UCI ML housing dataset.
http://archive.ics.uci.edu/ml/datasets/Housing
This dataset was taken from the StatLib library which is maintained at Carnegie Mellon University.
The Boston house-price data of Harrison, D. and Rubinfeld, D.L. 'Hedonic
prices and the demand for clean air', J. Environ. Economics & Management,
vol.5, 81-102, 1978. Used in Belsley, Kuh & Welsch, 'Regression diagnostics
...', Wiley, 1980. N.B. Various transformations are used in the table on
pages 244-261 of the latter.
The Boston house-price data has been used in many machine learning papers that address regression
problems.
**References**
- Belsley, Kuh & Welsch, 'Regression diagnostics: Identifying Influential Data and Sources of Collinearity', Wiley, 1980. 244-261.
- Quinlan,R. (1993). Combining Instance-Based and Model-Based Learning. In Proceedings on the Tenth International Conference of Machine Learning, 236-243, University of Massachusetts, Amherst. Morgan Kaufmann.
- many more! (see http://archive.ics.uci.edu/ml/datasets/Housing)
data = pd.DataFrame(boston.data, columns=boston.feature_names)
data.head()
| CRIM | ZN | INDUS | CHAS | NOX | RM | AGE | DIS | RAD | TAX | PTRATIO | B | LSTAT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 0 | 0.00632 | 18 | 2.31 | 0 | 0.538 | 6.575 | 65.2 | 4.0900 | 1 | 296 | 15.3 | 396.90 | 4.98 |
| 1 | 0.02731 | 0 | 7.07 | 0 | 0.469 | 6.421 | 78.9 | 4.9671 | 2 | 242 | 17.8 | 396.90 | 9.14 |
| 2 | 0.02729 | 0 | 7.07 | 0 | 0.469 | 7.185 | 61.1 | 4.9671 | 2 | 242 | 17.8 | 392.83 | 4.03 |
| 3 | 0.03237 | 0 | 2.18 | 0 | 0.458 | 6.998 | 45.8 | 6.0622 | 3 | 222 | 18.7 | 394.63 | 2.94 |
| 4 | 0.06905 | 0 | 2.18 | 0 | 0.458 | 7.147 | 54.2 | 6.0622 | 3 | 222 | 18.7 | 396.90 | 5.33 |
Но огромные таблицы, особенно если признаков очень много, сложно анализировать:
data.corr()
| CRIM | ZN | INDUS | CHAS | NOX | RM | AGE | DIS | RAD | TAX | PTRATIO | B | LSTAT | |
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CRIM | 1.000000 | -0.199458 | 0.404471 | -0.055295 | 0.417521 | -0.219940 | 0.350784 | -0.377904 | 0.622029 | 0.579564 | 0.288250 | -0.377365 | 0.452220 |
| ZN | -0.199458 | 1.000000 | -0.533828 | -0.042697 | -0.516604 | 0.311991 | -0.569537 | 0.664408 | -0.311948 | -0.314563 | -0.391679 | 0.175520 | -0.412995 |
| INDUS | 0.404471 | -0.533828 | 1.000000 | 0.062938 | 0.763651 | -0.391676 | 0.644779 | -0.708027 | 0.595129 | 0.720760 | 0.383248 | -0.356977 | 0.603800 |
| CHAS | -0.055295 | -0.042697 | 0.062938 | 1.000000 | 0.091203 | 0.091251 | 0.086518 | -0.099176 | -0.007368 | -0.035587 | -0.121515 | 0.048788 | -0.053929 |
| NOX | 0.417521 | -0.516604 | 0.763651 | 0.091203 | 1.000000 | -0.302188 | 0.731470 | -0.769230 | 0.611441 | 0.668023 | 0.188933 | -0.380051 | 0.590879 |
| RM | -0.219940 | 0.311991 | -0.391676 | 0.091251 | -0.302188 | 1.000000 | -0.240265 | 0.205246 | -0.209847 | -0.292048 | -0.355501 | 0.128069 | -0.613808 |
| AGE | 0.350784 | -0.569537 | 0.644779 | 0.086518 | 0.731470 | -0.240265 | 1.000000 | -0.747881 | 0.456022 | 0.506456 | 0.261515 | -0.273534 | 0.602339 |
| DIS | -0.377904 | 0.664408 | -0.708027 | -0.099176 | -0.769230 | 0.205246 | -0.747881 | 1.000000 | -0.494588 | -0.534432 | -0.232471 | 0.291512 | -0.496996 |
| RAD | 0.622029 | -0.311948 | 0.595129 | -0.007368 | 0.611441 | -0.209847 | 0.456022 | -0.494588 | 1.000000 | 0.910228 | 0.464741 | -0.444413 | 0.488676 |
| TAX | 0.579564 | -0.314563 | 0.720760 | -0.035587 | 0.668023 | -0.292048 | 0.506456 | -0.534432 | 0.910228 | 1.000000 | 0.460853 | -0.441808 | 0.543993 |
| PTRATIO | 0.288250 | -0.391679 | 0.383248 | -0.121515 | 0.188933 | -0.355501 | 0.261515 | -0.232471 | 0.464741 | 0.460853 | 1.000000 | -0.177383 | 0.374044 |
| B | -0.377365 | 0.175520 | -0.356977 | 0.048788 | -0.380051 | 0.128069 | -0.273534 | 0.291512 | -0.444413 | -0.441808 | -0.177383 | 1.000000 | -0.366087 |
| LSTAT | 0.452220 | -0.412995 | 0.603800 | -0.053929 | 0.590879 | -0.613808 | 0.602339 | -0.496996 | 0.488676 | 0.543993 | 0.374044 | -0.366087 | 1.000000 |
Поэтому давайте визуализируем ее!
correlation = data.corr()
plt.figure(figsize=(6, 6))
plt.pcolor(correlation)
plt.xticks(np.arange(0.5, len(data.columns)), data.columns, rotation='vertical')
plt.yticks(np.arange(0.5, len(data.columns)), data.columns)
plt.colorbar()
<matplotlib.colorbar.Colorbar at 0x11b9e8f10>
Функция colorbar строит соответствие цвета и значения. Обратите внимание, что функция pcolor принимает на вход просто некоторую матрицу. Например, можно (зачем-то) визуализировать все признаки:
plt.pcolor(data.values)
plt.colorbar()
<matplotlib.colorbar.Colorbar at 0x11b9b2950>
Это называется "hotmap" – чем больше значение, тем "горячее" цвет.
Сэмплирование?¶
Хочется посмотреть на признак, но данных очень много. Давайте возьмем случайное подмножество точек и будем смотреть на них.
points = np.random.choice(data.AGE, 100)
Посмотрим на признаки повнимательнее¶
Как визуализировать один признак?
Например, набор точек на прямой
plt.figure(figsize=(15, 1.5)), plt.grid(True, axis='x'), plt.yticks([])
plt.scatter(points, np.zeros(points.shape[0]))
<matplotlib.collections.PathCollection at 0x110de51d0>
Недостатки: не видно плотности точек в некоторых участках.
Что с этим можно сделать? Например, для каждой точки выберем случайно вертикальную координату (jitter)
plt.figure(figsize=(15, 1.5)), plt.grid(True, axis='x'), plt.yticks([])
plt.scatter(points, np.random.randn(points.shape[0]), marker='*', s=50)
<matplotlib.collections.PathCollection at 0x121d67550>
Можно построить гистограмму:
plt.hist(points)
(array([ 1., 6., 14., 6., 7., 8., 3., 9., 13., 33.]),
array([ 7.8 , 17.02, 26.24, 35.46, 44.68, 53.9 , 63.12,
72.34, 81.56, 90.78, 100. ]),
<a list of 10 Patch objects>)
При этом если признаков несколько, то можно их все построить на одной гистограмме:
random_indexies = np.random.choice(data.index, 100)
tot_points = data['RM'][random_indexies]
other_points = data['DIS'][random_indexies]
free_points = data['LSTAT'][random_indexies]
plt.hist([tot_points, other_points, free_points])
plt.legend(('RM', 'DIS', 'LSTAT'), loc='upper right')
<matplotlib.legend.Legend at 0x1189e6090>
Но вернемся к одному признаку.
Альтернатива диаграмме — KDE (Kernel Density Estimation).
Значение графика в точке: $f(x) = \dfrac{1}{nh}\sum_{i=1}^n{K(\dfrac{x - x_i}{h})}$
from scipy.stats import gaussian_kde
density = gaussian_kde(points)
xs = np.linspace(min(points)-0.01, max(points)+0.01, 100)
plt.plot(xs, density(xs), linewidth=2.5, color='red')
plt.scatter(points, np.zeros(len(points)), s=50, alpha=0.4)
<matplotlib.collections.PathCollection at 0x121ce33d0>
Однако здесь аналогичные проблемы, что и у гистограммы: выбор "шага"
density = gaussian_kde(points, bw_method=0.1)
xs = np.linspace(min(points)-0.01, max(points)+0.01, 100)
plt.plot(xs, density(xs), linewidth=2.5, color='red')
plt.scatter(points, np.zeros(len(points)), s=50, alpha=0.4)
<matplotlib.collections.PathCollection at 0x11f7eded0>
density = gaussian_kde(points, bw_method=4)
xs = np.linspace(min(points)-0.01, max(points)+0.01, 100)
plt.plot(xs, density(xs), linewidth=2.5, color='red')
plt.scatter(points, np.zeros(len(points)), s=50, alpha=0.4)
<matplotlib.collections.PathCollection at 0x11bf79f10>
Ящик с усами (диаграмма размаха)¶

Первый ($Q_1$) и третий ($Q_3$) квартили — концы ящика, медиана (второй квартиль) — вертикальная линия внутри ящика, усы — $Q_1 - 1.5 * IQR$ и $Q_3 + 1.5 * IQR$, $IQR$ = interquartile range, $Q_3 - Q_1$, остальные точки — выбросы. Иногда усы строят чуть по-другому.
_ = data[['RM', 'DIS', 'LSTAT']].boxplot()
/usr/local/lib/python2.7/site-packages/ipykernel/__main__.py:1: FutureWarning: The default value for 'return_type' will change to 'axes' in a future release. To use the future behavior now, set return_type='axes'. To keep the previous behavior and silence this warning, set return_type='dict'. if __name__ == '__main__':
Два признака¶
Scatter Matrix - скаттеры для каждой пары признаков
На диагонали матрицы стоит гистограмма или kde (параметр diagonal).
from sklearn import datasets
from pandas.tools.plotting import scatter_matrix
iris = datasets.load_iris()
data = pd.DataFrame(iris['data'], columns=iris['feature_names'])
c = ["red", "green", "blue"]
colors = [c[i] for i in iris['target']]
_ = scatter_matrix(data, figsize=(16, 16), diagonal='kde', s=200, c=colors)
Дискретные признаки¶
Для начала просто дискретизуем признаки.
f = (iris.data[:,3] - min(iris.data[:,3]))*4
feature = np.zeros(len(f))
feature[f > 1.5] = 1
feature[f > 2] = 2
feature[f > 6] = 3
Теперь изобразим их просто скаттером.
plt.scatter(np.zeros(feature.shape[0]), feature)
<matplotlib.collections.PathCollection at 0x11b7df2d0>
Кажется для дискретных признаков эта визуализация не очень информативна. Поэтому используем уже знакомый нам подход – сделаем jitter.
plt.figure(figsize=(12, 7))
plt.scatter(np.random.randn(len(feature)), feature, alpha=0.5, c=iris.target, s=100)
plt.grid(True)
Модель линейной регрессии.¶
Обучающая выборка: $x_i$ — объект ($\mathbb{R}^k$), $y_i$ — ответ ($\mathbb{R}$)
$X^l = \{(x_i, y_i)\}_{i=1}^l$
Пытаемся восстановить неизвестную зависимость $a(x) = f(x, w)$, где $w \in \mathbb{R}^p$ — параметры, $f$ — выбранное семейство функций.
Предполагаем, что $y(x) \approx a(x)$
Задача сводится к нахождению $w$.
Метод наименьших квадратов¶
$Q(w, X) = \sum_{i=1}^l(f(x_i; w) - y_i)^2 \to \min_{w}$
Линейная регрессия¶
$f(x; w) = \sum_{i=1}^n w_i * x_i + w_0 = \langle w, x\rangle$ (добавляем константный признак к данным)
В двумерном пространстве соответствует прямой на плоскости.
Аналитическое решение¶
$w = (X^TX)^{-1}X^Ty$
Для начала разделим все данные на обучающие и тестовые.
from sklearn.cross_validation import train_test_split
X_train, X_test, y_train, y_test = train_test_split(boston.data, boston.target,
random_state=241, test_size=0.2)
Обучим модель линейной регрессии:
from sklearn.linear_model import LinearRegression
?LinearRegression
У всех алгоритмов машинного обучения в библиотеке sklearn похожий интерфейс:
- для начала нужно создать классификатор (и задать параметры, если требуется)
- обучить модель необходимо вызвать метод fit, передав на вход матрицу с признаками и столбец ответов
- для применения модели необходимо вызвать метод predict
lr = LinearRegression()
lr.fit(X_train, y_train)
LinearRegression(copy_X=True, fit_intercept=True, n_jobs=1, normalize=False)
Как мерить качество?
Например, с помощью $MSE = \dfrac{1}{l}\sum_{i=1}^l{(a(x_i) - y_i)^2}$ или $MAE = \dfrac{1}{l}\sum_{i=1}^l{|a(x_i) - y_i|}$
Эти метрики уже реализованы в sklearn в модуле metrics:
from sklearn.metrics import mean_squared_error, mean_absolute_error
mean_absolute_error(y_test, lr.predict(X_test))
3.39
mean_squared_error(y_test, lr.predict(X_test))
27.37
Как понять: 27 — это много или мало?
Можно ввести "нормированный" MSE — коэффициент детерминации:
$R^2 = 1 - \dfrac{\sum_{i=1}^l{(a(x_i) - y_i)^2}}{\sum_{i=1}^l{(y_i - \bar{y})^2}}$, где $\bar{y} = \dfrac{1}{l}\sum_{i=1}^l y_i$
Его уже можно интерпретировать:
- $R^2 \approx 1$ — отлично
- $R^2 \approx 0$ — плохо
- $R^2 < 0$ — ужасно
from sklearn.metrics import r2_score
r2_score(y_test, lr.predict(X_test))
0.66
В чем недостаток тукущего способа оценки качества? Если немного поменять разбиение выборки на обучающую/тестовую, то качество может сильно измениться!
X_train, X_test, y_train, y_test = train_test_split(boston.data, boston.target, random_state=13, test_size=0.2)
lr = LinearRegression()
lr.fit(X_train, y_train)
print mean_absolute_error(y_test, lr.predict(X_test))
print mean_squared_error(y_test, lr.predict(X_test))
print r2_score(y_test, lr.predict(X_test))
3.64186894464 24.3636130537 0.731266198822
Что делать в этом случае? Можно несколько раз разбить выборку на обучающую/тестовую, и итоговым качеством алгоритма считать среднее качество. Этот подходи называетс K-fold.
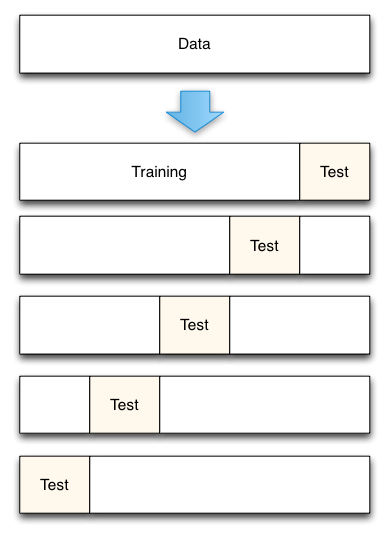
Kfold также реализован в sklearn. Его обязательный параметр: размер выборки. Дальше вы можете по желанию указать количество фолдов (n_folds), и перемешивать ли данные (shuffle). В результате этот объект возвращает заданное количество (n_folds) количество пар индексов: для обучающей и тестовой выборки.
from sklearn.cross_validation import KFold
kFold = KFold(boston.target.shape[0], n_folds=5, shuffle=True, random_state=42)
def get_quality(regressor, X, y, kFold):
metrics = {'mae': [], 'mse': [], 'r2': []}
for train, test in kFold:
regressor.fit(X[train], y[train])
predict = regressor.predict(X[test])
metrics['mae'].append(mean_absolute_error(y[test], predict))
metrics['mse'].append(mean_squared_error(y[test], predict))
metrics['r2'].append(r2_score(y[test], predict))
return metrics
for metric, scores in get_quality(LinearRegression(), boston.data, boston.target, kFold).iteritems():
print metric, np.mean(scores), np.std(scores)
mse 23.4932551603 1.84246315657 mae 3.39074777444 0.183852969097 r2 0.715147097604 0.037602797767
Чтобы можно было проинтерпретировать веса линейной модели, необходимо масштабировать данные. Например модифицируем данные таким образом, что:
- среднее равно 0
- среднеквадратичное отклонение равно 1
from sklearn.preprocessing import StandardScaler
scaler = StandardScaler()
scaler.fit(boston.data)
scaled_data = scaler.transform(boston.data)
scaled_data
array([[-0.41771335, 0.28482986, -1.2879095 , ..., -1.45900038,
0.44105193, -1.0755623 ],
[-0.41526932, -0.48772236, -0.59338101, ..., -0.30309415,
0.44105193, -0.49243937],
[-0.41527165, -0.48772236, -0.59338101, ..., -0.30309415,
0.39642699, -1.2087274 ],
...,
[-0.41137448, -0.48772236, 0.11573841, ..., 1.17646583,
0.44105193, -0.98304761],
[-0.40568883, -0.48772236, 0.11573841, ..., 1.17646583,
0.4032249 , -0.86530163],
[-0.41292893, -0.48772236, 0.11573841, ..., 1.17646583,
0.44105193, -0.66905833]])
np.mean(scaled_data, axis=0)
array([ 6.34099712e-17, -6.34319123e-16, -2.68291099e-15,
4.70199198e-16, 2.49032240e-15, -1.14523016e-14,
-1.40785495e-15, 9.21090169e-16, 5.44140929e-16,
-8.86861950e-16, -9.20563581e-15, 8.16310129e-15,
-3.37016317e-16])
lr = LinearRegression().fit(scaled_data, boston.target)
for feature, coef in sorted(zip(boston.feature_names, lr.coef_), key=lambda x: abs(x[1]), reverse=True):
print feature, coef
LSTAT -3.74867981912 DIS -3.10444805148 RM 2.67064141332 RAD 2.65878654091 TAX -2.07589814093 PTRATIO -2.06215592597 NOX -2.06009246354 ZN 1.08098057817 CRIM -0.9204111277 B 0.856640435817 CHAS 0.682203460284 INDUS 0.14296712402 AGE 0.0211206306213
Иногда после обучения линейной модели получаются слишком большие веса. Обычно это свидетельствует о переобучении. Поэтому в модель вводят регуляризацию, то есть штраф на слишком большие значения весов.
Ridge regression¶
Например, так называемый $L_2$ регуляризатор — квадрат $L_2$ нормы вектора весов:
$\left\lVert w \right\rVert_2^2 = \sum_{j=1}^p w^2$
Теперь задача будет иметь следующий вид:
$Q(w, X) = \sum_{i=1}^l(f(x_i; w) - y_i)^2 + \alpha_2 \left\lVert w \right\rVert_2^2 \to \min_{w}$
from sklearn.linear_model import Ridge
for metric, scores in get_quality(Ridge(alpha=10), scaled_data, boston.target, kFold).iteritems():
print metric, np.mean(scores), np.std(scores)
mse 23.5647341986 1.95053677092 mae 3.35621197703 0.201701366897 r2 0.714360180038 0.0377762819421
Остался вопрос как подбирать $\alpha$? И что это вообще такое?
В алгоритмах машинного обучения следует различать параметры модели и гиперпараметры (структурные параметры). Обычно параметры модели настраиваются в ходе обучения (например, веса в линейной модели), в то время как гиперпараметры задаются заранее (например, $\alpha$ в регуляризованной линейной модели). Каждая модель обычно имеет множество гиперпараметров, и нет универсальных наборов гиперпараметров, оптимально работающих во всех задачах, для каждой задачи нужно подбирать свой набор.
Для оптимизации гиперпараметров модели часто используют перебор по сетке (grid search): для каждого гиперпараметра выбирается несколько значений, перебираются все комбинации значений и выбирается комбинация, на которой модель показывает лучшее качество (с точки зрения метрики, которая оптимизируется). Однако в этом случае нужно грамотно оценивать построенную модель, а именно делать разбиение на обучающую и тестовую выборку. Есть несколько схем, как это можно реализовать:
- Разбить имеющуюся выборку на обучающую и тестовую. В этом случае сравнение большого числа моделей при переборе параметров приводит к ситуации, когда лучшая на тестовой подвыборке модель не сохраняет свои качества на новых данных. Можно сказать, что происходит переобучение на тестовую выборку.
- Для устранения описанной выше проблемы, можно разбить данные на 3 непересекающихся подвыборки: обучение (train), валидация (validation) и контроль (test). Валидационную подвыборку используют для сравнения моделей, а test — для окончательной оценки качества и сравнения семейств моделей с подобранными параметрами.
- Другой способ сравнения моделей — кросс-валидация. Существуют различные схемы кросс-валидации:
- Leave-One-Out (убираем из выборки один объект, обучаемся на оставшейся, предсказываем качество на убранном объекте)
- K-Fold
- Многократное случайное разбиение выборки
Для Ridge-регрессии реализован специальный класс, позволяющий подобрать оптимальное $\alpha$.
from sklearn.linear_model import RidgeCV
rcv = RidgeCV(alphas=(0.01, 0.1, 1.0), cv=kFold)
rcv.fit(scaled_data, boston.target)
rcv.alpha_
1.00
for metric, scores in get_quality(Ridge(alpha=1.0), scaled_data, boston.target, kFold).iteritems():
print metric, np.mean(scores), np.std(scores)
mse 23.4927932848 1.85542596288 mae 3.3855230191 0.185203170524 r2 0.715158625182 0.0376359203817
Lasso regression¶
$\left\lVert w \right\rVert_1 = \sum_{j=1}^p |w|$
Теперь задача будет иметь следующий вид:
$Q(w, X) = \sum_{i=1}^l(f(x_i; w) - y_i)^2 + \alpha_1 \left\lVert w \right\rVert_1 \to \min_{w}$
Качество в данном случае получилось немного меньше, в чем дело? После введения регуляризатора модель становится чувствительной к масштабу.
from sklearn.linear_model import Lasso, LassoCV
rcv = LassoCV(alphas=(0.001, 0.01, 0.1, 1.0, 10.0), cv=kFold)
rcv.fit(scaled_data, boston.target)
rcv.alpha_
0.01
for metric, scores in get_quality(Lasso(alpha=0.01), scaled_data, boston.target, kFold).iteritems():
print metric, np.mean(scores), np.std(scores)
mse 23.4845738831 1.86459144401 mae 3.38158579565 0.186140273659 r2 0.715250581386 0.0377123576456
Особенность $L_1$ регуляризатора в том, что он "отбирает признаки": зануляет коэффициенты перед некоторыми "неважными" признаками. Например:
lasso = Lasso(alpha=0.01).fit(scaled_data, boston.target)
lasso.coef_
array([-0.89, 1.04, 0.05, 0.68, -1.98, 2.68, 0. , -3.06, 2.48,
-1.9 , -2.04, 0.85, -3.74])
ElasticNet¶
$Q(w, X) = \sum_{i=1}^l(f(x_i; w) - y_i)^2 + \alpha_1 \left\lVert w \right\rVert_1 + \alpha_2 \left\lVert w \right\rVert_2^2\to \min_{w}$